
1-金刚烷乙酸 98%_A800984-5g
A800984-5g
-
原厂型号
-
-
品牌
-
单件重量
-
货期
无参数


A800984-5g
原厂型号
品牌
单件重量
货期
无参数
上海金畔生物科技有限公司代理AAT Bioquest荧光染料全线产品,欢迎访问AAT Bioquest荧光染料官网了解更多信息。
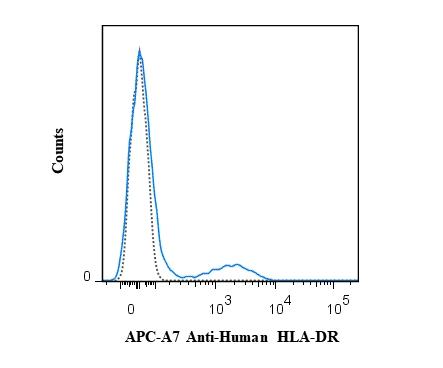 |
货号 | 1039 | 存储条件 | 在零下15度以下保存, 避免光照 |
| 规格 | 1 mg | 价格 | 2604 | |
| Ex (nm) | 762 | Em (nm) | 782 | |
| 分子量 | 1288.58 | 溶剂 | DMSO | |
| 产品详细介绍 | ||||
简要概述
iFluor A7 SE是iFluor系列荧光标记染料之一,可以覆盖整个可见光谱。所有iFluor 染料都具有优异的水溶性。它们的亲水性使有机溶剂的使用极小化。iFluor 染料也具有比经典荧光标记染料更好的标记性能,如FITC,TRITC,Texas Red ,Cy3 ,Cy5和Cy7。一些iFluor 染料在某些抗体上明显优于Alexa Fluor 标记染料。它们是用于标记蛋白质和核酸而不包含性能的极便宜的荧光染料(替代Alexa Fluor 染料)。每种iFluor染料的开发都与特定的Alexa Fluor 或其他标记染料(如DyLight 染料)的光谱特性相匹配。
琥珀酰亚胺基(NHS)酯被证明是用于胺修饰的极佳试剂,因为形成的酰胺键基本上与天然肽键相同并且稳定。这些试剂通常是稳定的并且与脂族胺显示出良好的反应性和选择性。当琥珀酰亚胺酯化合物用于缀合反应时,需要考虑的因素很少:1.溶剂:在大多数情况下,活性染料应溶于无水二甲基甲酰胺(DMF)或二甲基亚砜(DMSO)中。 2.反应pH:胺与琥珀酰亚胺酯的标记反应强烈依赖于pH。胺反应性试剂与非质子化脂族胺基团反应,包括蛋白质的末端胺和赖氨酸的β-氨基。因此,胺酰化反应通常在pH 7.5以上进行。通过琥珀酰亚胺酯进行的蛋白质修饰通常可以在pH 8.5-9.5下进行。 3.反应缓冲液:使用胺反应试剂时,必须避免使用含有游离胺(如Tris和甘氨酸)和硫醇化合物的缓冲液。广泛用于蛋白质沉淀的铵盐(例如硫酸铵和乙酸铵)也必须在进行染料缀合之前除去(例如通过透析)。 4.反应温度:大多数缀合在室温下进行。特定标记反应可能需要升高或降低的温度。iFluor系列染料是AF系列染料的完美替代品。

点击查看光谱
点击查看实验方案
产品说明书
染色样本分析
操作步骤
1.准备蛋白质储备溶液(溶液A):
将100μL反应缓冲液(如1 M碳酸钠溶液或1 M磷酸盐缓冲液,pH~9.0)与900μL目标蛋白溶液(如抗体,蛋白质浓度> 2 mg / ml,如果可能)混合至100μL给予1 mL蛋白质标记原液。
注1:蛋白质溶液(溶液A)的pH值应为8.5±0.5。如果蛋白质溶液的pH低于8.0,则使用1M碳酸氢钠溶液或1M pH 9.0磷酸盐缓冲液将pH调节至8.0-9.0的范围。
注2:蛋白质应溶解于pH7.2-7.4的1X磷酸盐缓冲盐水(PBS)中。如果蛋白质溶解在Tris或甘氨酸缓冲液中,则必须用pH7.2-7.4的1X PBS透析,以除去广泛用于蛋白质沉淀的游离胺或铵盐(例如硫酸铵和乙酸铵)。
注3:不纯的抗体、稳定的牛血清蛋白(BSA)抗体或明胶不会被很好的标记。叠氮化钠或硫柳汞的存在也可能干扰缀合反应。可以通过透析或旋转柱除去叠氮化钠或硫柳汞,以获得极佳标记结果。
注4:如果蛋白质浓度低于2 mg / mL,则结合效率会显着降低。为获得极佳标记效率,建议极终蛋白质浓度范围为2-10 mg / mL。
2.准备染料储备溶液(溶液B):
将无水DMSO加入到iFluor 染料SE小瓶中以制备10-20mM储备溶液。 通过移液或涡旋混合均匀。
注意:在开始缀合前准备染料储备溶液(溶液B)。 及时使用。 染料储备溶液的长期储存可降低染料活性。 溶液B可在冰箱中保存两周,避光保存。 避免冻融循环。
3.确定极佳染料/蛋白质比例(可选):
注意:每种蛋白质都需要不同的染料/蛋白质比例,这也取决于染料的性质。蛋白质的过度标记可能不利地影响其结合亲和力,而低染料/蛋白质比率的蛋白质缀合物会降低灵敏度。我们建议您通过使用连续不同量的标记染料溶液重复步骤4和5来实验确定极佳染料/蛋白质比率。通常,对于大多数染料 – 蛋白质缀合物,推荐使用4-6种染料/蛋白质。
3.1使用10:1摩尔比的溶液B(染料)/溶液A(蛋白质)作为起始点:将5μl染料储备溶液(溶液B,假设染料储备溶液为10 mM)加入到样品瓶中。蛋白质溶液(95μl溶液A)有效摇动。假设蛋白质浓度为10mg / mL并且蛋白质的分子量为~200KD,蛋白质的浓度为~0.05mM。
注意:蛋白质溶液中DMSO的浓度应<10%。
3.2运行缀合反应(参见下面的步骤4)。
3.3重复#3.2,溶液B /溶液A的摩尔比为5:1;分别为15:1和20:1。
3.4使用预制的旋转柱纯化所需的缀合物。
3.5计算上述4种结合物的染料/蛋白质比(DOS)(见说明书)。
3.6运行上述4种结合物的功能测试,确定极佳的染料/蛋白质比例,以扩大标记反应。
4.运行结合反应:
4.1有效加入适量的染料储备溶液(溶液B)到蛋白质溶液(溶液A)的小瓶中晃动。
注意:溶液B /溶液的极佳摩尔比由步骤3.6确定。如果跳过步骤3,我们建议使用10:1溶液B(染料)/溶液A(蛋白质)的摩尔比。
4.2继续在室温下旋转或摇动反应混合物30-60分钟。
5.纯化缀合物
以下方案是使用Sephadex G-25柱纯化染料 – 蛋白质缀合物的实例。
5.1按照制造说明准备Sephadex G-25色谱柱。
5.2将反应混合物(直接从步骤4)加载到Sephadex G-25柱的顶部。
5.3样品在顶部树脂表面下方运行时立即加入PBS(pH 7.2-7.4)。
5.4向所需样品中加入更多PBS(pH 7.2-7.4)以完成色谱柱纯化。 合并含有所需染料 – 蛋白质缀合物的级分。
注1:立即使用时,染料 – 蛋白质偶联物需要用染色缓冲液稀释,并等分多次使用。
注2:对于长期储存,染料 – 蛋白质缀合物溶液需要浓缩或冷冻干燥
参考文献
Deep Sequencing Analysis of the Eha-Regulated Transcriptome of Edwardsiella tarda Following Acidification
Authors: D Gao, N Liu, Y Li, Y Zhang, G Liu
Journal: Metabolomics (Los Angel) (2017): 2153–0769
Suramin inhibits cullin-RING E3 ubiquitin ligases
Authors: Kenneth Wu, Robert A Chong, Qing Yu, Jin Bai, Donald E Spratt, Kevin Ching, Chan Lee, Haibin Miao, Inger Tappin, Jerard Hurwitz
Journal: Proceedings of the National Academy of Sciences (2016): E2011–E2018
Glycosaminoglycan mimicry by COAM reduces melanoma growth through chemokine induction and function
Authors: Helene Piccard, Nele Berghmans, Eva Korpos, Chris Dillen, Ilse Van Aelst, Sandra Li, Erik Martens, Sandra Liekens, Sam Noppen, Jo Van Damme
Journal: International Journal of Cancer (2012): E425–E436
上海金畔生物科技有限公司代理AAT Bioquest荧光染料全线产品,欢迎访问AAT Bioquest荧光染料官网了解更多信息。
 |
货号 | 71517 | 存储条件 | 在零下15度以下保存, 避免光照 |
| 规格 | 5 mg | 价格 | 9180 | |
| Ex (nm) | 762 | Em (nm) | 782 | |
| 分子量 | 1288.58 | 溶剂 | DMSO | |
| 产品详细介绍 | ||||
简要概述
iFluor A7 SE是iFluor系列荧光标记染料之一,可以覆盖整个可见光谱。所有iFluor 染料都具有优异的水溶性。它们的亲水性使有机溶剂的使用极小化。iFluor 染料也具有比经典荧光标记染料更好的标记性能,如FITC,TRITC,Texas Red ,Cy3 ,Cy5和Cy7。一些iFluor 染料在某些抗体上明显优于Alexa Fluor 标记染料。它们是用于标记蛋白质和核酸而不包含性能的极便宜的荧光染料(替代Alexa Fluor 染料)。每种iFluor染料的开发都与特定的Alexa Fluor 或其他标记染料(如DyLight 染料)的光谱特性相匹配。
琥珀酰亚胺基(NHS)酯被证明是用于胺修饰的极佳试剂,因为形成的酰胺键基本上与天然肽键相同并且稳定。这些试剂通常是稳定的并且与脂族胺显示出良好的反应性和选择性。当琥珀酰亚胺酯化合物用于缀合反应时,需要考虑的因素很少:1.溶剂:在大多数情况下,活性染料应溶于无水二甲基甲酰胺(DMF)或二甲基亚砜(DMSO)中。 2.反应pH:胺与琥珀酰亚胺酯的标记反应强烈依赖于pH。胺反应性试剂与非质子化脂族胺基团反应,包括蛋白质的末端胺和赖氨酸的β-氨基。因此,胺酰化反应通常在pH 7.5以上进行。通过琥珀酰亚胺酯进行的蛋白质修饰通常可以在pH 8.5-9.5下进行。 3.反应缓冲液:使用胺反应试剂时,必须避免使用含有游离胺(如Tris和甘氨酸)和硫醇化合物的缓冲液。广泛用于蛋白质沉淀的铵盐(例如硫酸铵和乙酸铵)也必须在进行染料缀合之前除去(例如通过透析)。 4.反应温度:大多数缀合在室温下进行。特定标记反应可能需要升高或降低的温度。iFluor系列染料是AF系列染料的完美替代品。

点击查看实验方案
产品说明书
染色样本分析
操作步骤
1.准备蛋白质储备溶液(溶液A):
将100μL反应缓冲液(如1 M碳酸钠溶液或1 M磷酸盐缓冲液,pH~9.0)与900μL目标蛋白溶液(如抗体,蛋白质浓度> 2 mg / ml,如果可能)混合至100μL给予1 mL蛋白质标记原液。
注1:蛋白质溶液(溶液A)的pH值应为8.5±0.5。如果蛋白质溶液的pH低于8.0,则使用1M碳酸氢钠溶液或1M pH 9.0磷酸盐缓冲液将pH调节至8.0-9.0的范围。
注2:蛋白质应溶解于pH7.2-7.4的1X磷酸盐缓冲盐水(PBS)中。如果蛋白质溶解在Tris或甘氨酸缓冲液中,则必须用pH7.2-7.4的1X PBS透析,以除去广泛用于蛋白质沉淀的游离胺或铵盐(例如硫酸铵和乙酸铵)。
注3:不纯抗体、牛血清白蛋白(BSA)或明胶稳定的抗体不会被很好地标记。叠氮化钠或硫柳汞的存在也可能干扰缀合反应。可以通过透析或旋转柱除去叠氮化钠或硫柳汞,以获得极佳标记结果。
注4:如果蛋白质浓度低于2 mg / mL,则结合效率会显着降低。为获得极佳标记效率,建议极终蛋白质浓度范围为2-10 mg / mL。
2.准备染料储备溶液(溶液B):
将无水DMSO加入到iFluor 染料SE小瓶中以制备10-20mM储备溶液。 通过移液或涡旋混合均匀。
注意:在开始缀合前准备染料储备溶液(溶液B)。 及时使用。 染料储备溶液的长期储存可降低染料活性。 溶液B可在冰箱中保存两周,避光保存。 避免冻融循环。
3.确定极佳染料/蛋白质比例(可选):
注意:每种蛋白质都需要不同的染料/蛋白质比例,这也取决于染料的性质。蛋白质的过度标记可能不利地影响其结合亲和力,而低染料/蛋白质比率的蛋白质缀合物会降低灵敏度。我们建议您通过使用连续不同量的标记染料溶液重复步骤4和5来实验确定极佳染料/蛋白质比率。通常,对于大多数染料 – 蛋白质缀合物,推荐使用4-6种染料/蛋白质。
3.1使用10:1摩尔比的溶液B(染料)/溶液A(蛋白质)作为起始点:将5μl染料储备溶液(溶液B,假设染料储备溶液为10 mM)加入到样品瓶中。蛋白质溶液(95μl溶液A)有效摇动。假设蛋白质浓度为10mg / mL并且蛋白质的分子量为~200KD,蛋白质的浓度为~0.05mM。
注意:蛋白质溶液中DMSO的浓度应<10%。
3.2运行缀合反应(参见下面的步骤4)。
3.3重复#3.2,溶液B /溶液A的摩尔比为5:1;分别为15:1和20:1。
3.4使用预制的旋转柱纯化所需的缀合物。
3.5计算上述4种结合物的染料/蛋白质比(DOS)(见说明书)。
3.6运行上述4种结合物的功能测试,确定极佳的染料/蛋白质比例,以扩大标记反应。
4.运行结合反应:
4.1有效加入适量的染料储备溶液(溶液B)到蛋白质溶液(溶液A)的小瓶中晃动。
注意:溶液B /溶液的极佳摩尔比由步骤3.6确定。如果跳过步骤3,我们建议使用10:1溶液B(染料)/溶液A(蛋白质)的摩尔比。
4.2继续在室温下旋转或摇动反应混合物30-60分钟。
5.纯化缀合物
以下方案是使用Sephadex G-25柱纯化染料 – 蛋白质缀合物的实例。
5.1按照制造说明准备Sephadex G-25色谱柱。
5.2将反应混合物(直接从步骤4)加载到Sephadex G-25柱的顶部。
5.3样品在顶部树脂表面下方运行时立即加入PBS(pH 7.2-7.4)。
5.4向所需样品中加入更多PBS(pH 7.2-7.4)以完成色谱柱纯化。 合并含有所需染料 – 蛋白质缀合物的级分。
注1:立即使用时,染料 – 蛋白质偶联物需要用染色缓冲液稀释,并等分多次使用。
注2:对于长期储存,染料 – 蛋白质缀合物溶液需要浓缩或冷冻干燥
参考文献
Deep Sequencing Analysis of the Eha-Regulated Transcriptome of Edwardsiella tarda Following Acidification
Authors: D Gao, N Liu, Y Li, Y Zhang, G Liu
Journal: Metabolomics (Los Angel) (2017): 2153–0769
Suramin inhibits cullin-RING E3 ubiquitin ligases
Authors: Kenneth Wu, Robert A Chong, Qing Yu, Jin Bai, Donald E Spratt, Kevin Ching, Chan Lee, Haibin Miao, Inger Tappin, Jerard Hurwitz
Journal: Proceedings of the National Academy of Sciences (2016): E2011–E2018
Glycosaminoglycan mimicry by COAM reduces melanoma growth through chemokine induction and function
Authors: Helene Piccard, Nele Berghmans, Eva Korpos, Chris Dillen, Ilse Van Aelst, Sandra Li, Erik Martens, Sandra Liekens, Sam Noppen, Jo Van Damme
Journal: International Journal of Cancer (2012): E425–E436
上海金畔生物科技有限公司代理AAT Bioquest荧光染料全线产品,欢迎访问AAT Bioquest荧光染料官网了解更多信息。
| 货号 | V101005 | 存储条件 | Multiple |
| 规格 | 96 Tests | 价格 | 2472 |
| Ex (nm) | Em (nm) | ||
| 分子量 | 溶剂 | ||
| 产品详细介绍 | |||
简要概述
用于定量测定血清/血浆样品和细胞培养上清液中的人类载脂蛋白A1(apoA1)。请注意,洗涤,封闭和孵育缓冲液应包含清洁剂。吐温20,Triton X-100或NP40的使用浓度为0.05-0.5%。在封闭缓冲液和孵育缓冲液中,建议使用0.1%BSA,而不要使用牛血清,因为HDL 44也可以结合牛apoA1。
血清/血浆样品:分析人血清/血浆样品时,建议使用Apo ELISA缓冲液稀释样品,标准品和检测抗体。该缓冲液可防止可能由于人血浆和血清中常见的嗜异性抗体的干扰而引起的假阳性读数。apoB分析所必需的样品的Triton X处理不会干扰apoA1分析。建议将血清/血浆样品稀释150,000x至200,000x,请参见https://www.mabtech.com/knowledge-center/apodilution的稀释指南。避免重复冻融循环,不要将样品保存在-20°C下。储存在-20°C的样品会产生错误的高apoA1值。
注意:该试剂盒中未提供Apo ELISA缓冲液。
试剂:抗体是在含有叠氮化钠(0.02%)的无菌过滤(0.2μm)PBS中提供的。链霉亲和素-HRP用0.1M Tris缓冲液和0.002%Kathon CG提供。
标准范围:0.6-40 ng / ml
产品说明书
样品实验方案
储备溶液配制
通过将小瓶4内试剂重新溶于含1%BSA的1 ml PBS中来制备apoA1标准品,不要搅拌,在室温下放置15分钟,然后涡旋振荡3s。得到的储备液为4μg/ ml,应立即使用或以等分试样的形式储存在-20°C下,以备将来使用。我们建议等分试样在初次使用后不要重新冷冻。为了进行测试,请使用标准范围作为指导来准备原液的稀释液。
操作步骤
上海金畔生物科技有限公司代理AAT Bioquest荧光染料全线产品,欢迎访问AAT Bioquest荧光染料官网了解更多信息。
| 货号 | 1812 | 存储条件 | 在零下15度以下保存, 避免光照 |
| 规格 | 1 mg | 价格 | 2604 |
| Ex (nm) | 499 | Em (nm) | 520 |
| 分子量 | 643.40 | 溶剂 | DMSO |
| 产品详细介绍 | |||
简要概述
产品基本信息
货号:1812
产品名称:Alpha Fluor 488 NHS酯
规格:1mg
储存条件:保存在冰箱-15℃干燥
保质期:12个月
产品物理化学光谱特性
分子量:643.40
外观:固体
溶剂:DMSO
激发波长(nm):499
发射波长(nm):520
产品介绍
Alpha Fluor 488 NHS酯(琥珀酰亚胺酯)与AlexaFluor®488NHS酯相同(AlexaFluor®是ThermoFisher的商标)。它是一种明亮的绿色荧光染料,最适合与488 nm氩激光器配合使用。Alpha Fluor 488染料在pH 4至pH 10下是水溶性和pH不敏感的。Alpha Fluor 488的NHS酯(或琥珀酰亚胺基酯)是最方便的胺反应形式,用于将该染料与蛋白质或抗体结合。
点击查看光谱
点击查看实验方案
参考文献
Development of new hCaM-Alexa Fluor(R) biosensors for a wide range of ligands
Authors: Velazquez-Lopez, I.; Leon-Cruz, E.; Pardo, J. P.; Sosa-Peinado, A.; Gonzalez-Andrade, M.
Journal: Anal Biochem (2017): 13-22
Synthetic Protocol for AFCS: A Biologically Active Fluorescent Castasterone Analog Conjugated to an Alexa Fluor 647 Dye
Authors: Winne, J. M.; Irani, N. G.; Van den Begin, J.; Madder, A.
Journal: Methods Mol Biol (2017): 21-Sep
Alteration of AMPA Receptor-Mediated Synaptic Transmission by Alexa Fluor 488 and 594 in Cerebellar Stellate Cells
Authors: Maroteaux, M.; Liu, S. J.
Journal: eNeuro (2016)
Alexa fluor-labeled fluorescent cellulose nanocrystals for bioimaging solid cellulose in spatially structured microenvironments
Authors: Grate, J. W.; Mo, K. F.; Shin, Y.; Vasdekis, A.; Warner, M. G.; Kelly, R. T.; Orr, G.; Hu, D.; Dehoff, K. J.; Brockman, F. J.; Wilkins, M. J.
Journal: Bioconjug Chem (2015): 593-601
A mouse monoclonal antibody against Alexa Fluor 647
Authors: Wuethrich, I.; Guillen, E.; Ploegh, H. L.
Journal: Monoclon Antib Immunodiagn Immunother (2014): 109-20
In vivo visualization of GL261-luc2 mouse glioma cells by use of Alexa Fluor-labeled TRP-2 antibodies
Authors: Fenton, K. E.; Martirosyan, N. L.; Abdelwahab, M. G.; Coons, S. W.; Preul, M. C.; Scheck, A. C.
Journal: Neurosurg Focus (2014): E12
Green tea catechins quench the fluorescence of bacteria-conjugated Alexa fluor dyes
Authors: Zhao, L.; Li, W.; Zhu, S.; Tsai, S.; Li, J.; Tracey, K. J.; Wang, P.; Fan, S.; Sama, A. E.; Wang, H.
Journal: Inflamm Allergy Drug Targets (2013): 308-14
Volume labeling with Alexa Fluor dyes and surface functionalization of highly sensitive fluorescent silica (SiO2) nanoparticles
Authors: Wang, W.; Nallathamby, P. D.; Foster, C. M.; Morrell-Falvey, J. L.; Mortensen, N. P.; Doktycz, M. J.; Gu, B.; Retterer, S. T.
Journal: Nanoscale (2013): 10369-75
Fluorescence of Alexa fluor dye tracks protein folding
Authors: Lindhoud, S.; Westphal, A. H.; Visser, A. J.; Borst, J. W.; van Mierlo, C. P.
Journal: PLoS One (2012): e46838
a Luo-acupoint) in the rat: a double-labeling study of cholera toxin subunit B conjugated with Alexa Fluor 488 and 594]
Authors: Cui, J. J.; Zhu, X. L.; Ji, C. F.; Jing, X. H.; Bai, W. Z., [Neuroanatomical basis of clinical joint application of “Jinggu” (BL 64, a source-acupoint) and “Dazhong” (KI 4
Journal: Zhen Ci Yan Jiu (2011): 262-7
相关产品
| 产品名称 | 货号 |
| iFluor 488琥珀酰亚胺酯 | Cat#1023 |
| AF 594 NHS酯 等同于Alexa Fluor 594 | Cat#1830 |
| AF 350 NHS酯 等同于Alexa Fluor 350 | Cat#1800 |